Verfahren der Genom-Editierung optimiert
Bio-News vom 24.01.2023
Im Zuge der Optimierung von Schlüsselverfahren der Genom-Editierung ist es Forscherinnen und Forschern in Heidelberg gelungen, die Effizienz von molekulargenetischen Methoden wie CRISPR/Cas9 zu steigern und ihre Anwendungsgebiete zu erweitern. Die gemeinsam mit Kollegen anderer Disziplinen weiterentwickelten Werkzeuge erlauben ein wirksames genetisches Screening zur Modellierung spezifischer Genmutationen. Zudem können nun auch bislang unerreichbare Sequenzen der DNA modifiziert werden.
Im Zuge der Optimierung von Schlüsselverfahren der Genom-Editierung ist es Forscherinnen und Forschern der Abteilung Entwicklungsbiologie / Entwicklungsphysiologie am Centre for Organismal Studies der Universität Heidelberg gelungen, die Effizienz von molekulargenetischen Methoden wie CRISPR/Cas9 und verwandten Systemen maßgeblich zu steigern sowie ihre Anwendungsgebiete zu erweitern.
Publikation:
K. Pakari, J. Wittbrodt, T. Thumberger
De novo PAM generation to reach initially inaccessible target sites for base editing
Development (2023)
DOI: 10.1242/dev.201115
Die von den Biowissenschaftlern gemeinsam mit Kollegen anderer Disziplinen weiterentwickelten Werkzeuge erlauben unter anderem ein wirksames genetisches Screening zur Modellierung spezifischer Genmutationen. Zudem können nun auch bislang unerreichbare Sequenzen der DNA modifiziert werden. Nach den Worten von Prof. Dr. Joachim Wittbrodt eröffnen sich damit weitreichende neue Arbeitsfelder in der Grundlagenforschung und der potentiellen therapeutischen Anwendung.
Genom-Editierung
Als Genom-Editierung wird die gezielte Veränderung von DNA mit molekulargenetischen Methoden bezeichnet. Sie kommt in der Pflanzen- und Tierzucht, aber auch in der medizinischen und biologischen Grundlagenforschung zum Einsatz.
Zu den gängigsten Verfahren gehören die „Genschere“ CRISPR/Cas9 und ihre als Base-Editoren bekannten Varianten. In beiden Fällen müssen Enzyme in den Kern der Zielzelle transportiert werden. Dort angelangt, schneidet das CRISPR/Cas9-System die DNA an einer gezielt ausgesuchten Stelle, so dass es zu einem Bruch des Doppelstranges kommt. Dort können anschließend neue DNA-Abschnitte eingefügt werden.
Einen ähnlichen molekularen Mechanismus nutzen Base-Editoren, durchtrennen jedoch den DNA-Doppelstrang nicht. Stattdessen tauscht ein an das Cas9-Protein gekoppeltes Enzym einzelne Grundbausteine des Erbguts – die Nukleotide – gezielt aus. In drei aufeinander aufbauenden Studien ist es dem Team von Prof. Wittbrodt gelungen, die Effizienz und Anwendungsreichweite dieser Methoden maßgeblich zu steigern.
Eine Herausforderung bei der Anwendung von CRISPR/Cas9 besteht darin, die dafür nötigen Cas9-Enzyme effizient in den Zellkern einzuschleusen. „Die Zelle verfügt über einen ausgeklügelten ‚Türsteher‘-Mechanismus. Er unterscheidet zwischen Proteinen, die in den Kern vordringen dürfen, und solchen, die im Zytoplasma verbleiben sollen“, erklärt Dr. Tinatini Tavhelidse-Suck aus dem Team von Prof. Wittbrodt. Den Zugang ermöglicht hier ein Anhang aus einigen wenigen Aminosäuren, der wie eine „Eintrittskarte“ funktioniert. Die Wissenschaftler haben nun eine Art generell gültige „VIP-Eintrittskarte“ gefunden, die damit ausgestattete Enzyme sehr schnell in den Kern passieren lässt. Sie hat die Bezeichnung „high efficiency-tag“, kurz „hei-tag“, erhalten.
Publikation:
T. Thumberger, T. Tavhelidse-Suck, J. A. Gutierrez-Triana, A. Cornean, R. Medert, B. Welz, M. Freichel, J. Wittbrodt
Boosting targeted genome editing using the hei-tag
eLife (2022)
DOI: 10.7554/eLife.70558
„Auch andere Proteine, die in den Kern der Zelle vordringen müssen, sind mit ‚hei-tag‘ erfolgreicher“, so die Schlussfolgerung von Dr. Thomas Thumberger, der ebenfalls am Centre for Organismal Studies (COS) forscht. In Zusammenarbeit mit Pharmakologen der Universität Heidelberg konnte das Forschungsteam zeigen, dass Cas9 in Verbindung mit der „hei-tag-Eintrittskarte“ nicht nur im Modellorganismus Medaka, dem Japanischen Reiskärpfling (Oryzias latipes), sondern auch in Zellkulturen von Säugetieren und Mausembryonen hoch-effizient gezielte Genomveränderungen ermöglicht.
Publikation:
A. Cornean, J. Gierten, B. Welz, J. L. Mateo, T. Thumberger, J. Wittbrodt
Precise in vivo functional analysis of DNA variants with base editing using ACEofBASEs target prediction
eLife (2022)
DOI: 10.7554/eLife.72124
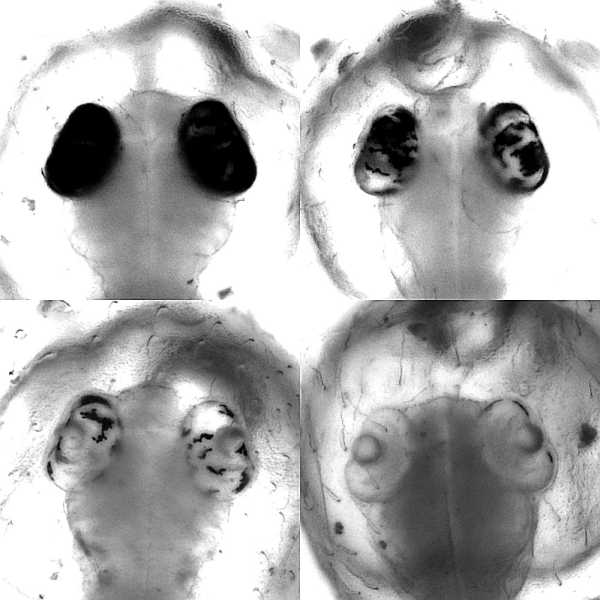
Dass Base-Editoren im lebenden Organismus mit großer Effizienz arbeiten und sich sogar für ein genetisches Screening eignen, haben die Heidelberger Wissenschaftler in einer weiteren Studie nachgewiesen. Im Versuch mit Japanischen Reiskärpflingen konnten sie zeigen, dass diese lokal begrenzten, gezielten Veränderungen einzelner DNA-Bausteine eine Wirkung entfalten, die sonst nur durch die vergleichsweise aufwändige Zucht von Organismen mit verändertem Erbgut erreicht wird. Das Forschungsteam am COS hat dabei in Zusammenarbeit mit Dr. Dr. Jakob Gierten, Kinderkardiologe am Universitätsklinikum Heidelberg, bestimmte Genmutationen in den Blick genommen.
Diese Mutationen standen im Verdacht, angeborene Herzfehler beim Menschen auszulösen. Durch die Veränderung einzelner DNA-Bausteine der entsprechenden Gene im Modellorganismus konnten die Wissenschaftler Fischembryonen mit den beschriebenen Herzfehlern nachahmen und studieren. Der gezielte Eingriff führte bereits in den frühen Embryonalstadien der Fische zu sichtbaren Veränderungen am Herzen, wie Doktorandin Bettina Welz und Dr. Alex Cornean, zwei der Erstautoren der Studie aus dem Team von Prof. Wittbrodt, ausführen. Dadurch konnten die Forscherinnen und Forscher den ursprünglichen Verdacht bestätigen und einen ursächlichen Zusammenhang zwischen genetischer Veränderung und Krankheitsbild herstellen.
Ermöglicht wurde der präzise Eingriff in das Erbgut der Fischembryonen durch die eigens entwickelte, online verfügbare Software ACEofBASEs. Damit lassen sich Stellen in Genen identifizieren, die sehr effizient zu gewünschten Veränderungen an den Zielgenen und daraus resultierenden Proteinen führen. Der Japanische Reiskärpfling ist dabei, so die Wissenschaftler, ein exzellenter genetischer Modellorganismus, um Mutationen zu modellieren, wie sie bei dem jeweiligen Patienten auftreten. „Unsere Methode ermöglicht eine effiziente Screening-Analyse und könnte damit einen Startpunkt für die Entwicklung individualisierter medizinischer Behandlung bieten“, so Jakob Gierten.
Mit den Einschränkungen von Base-Editoren befasst sich eine dritte Studie, die wiederum in der Arbeitsgruppe von Prof. Wittbrodt entstanden ist. Damit ein solcher Editor überhaupt an die DNA der Zielzelle binden kann, muss dort ein bestimmtes Sequenzmotiv vorhanden sein. Es trägt die Bezeichnung Protospacer Adjacent Motif, kurz PAM. „Fehlt dieses Motiv in der Nähe des zu verändernden DNA-Bausteins, ist ein Austausch von Nukleotiden unmöglich“, erklärt Dr. Thumberger. Ein Team unter seiner Leitung hat nun einen Weg gefunden, diese Einschränkung zu umgehen.
Dabei werden zwei Base-Editoren in einer einzelnen Zelle zeitlich nacheinander genutzt. In einem ersten Schritt wird ein neues DNA-Bindemotiv für einen weiteren Base-Editor erzeugt, woraufhin dieser zweite, gleichzeitig applizierte Editor eine Stelle editieren kann, die zuvor unerreichbar war. Dieser verschachtelte Gebrauch stellte sich als hoch effizient heraus, wie Kaisa Pakari, Erstautorin der Studie, erläutert. Mit diesem Kniff konnten die Heidelberger Wissenschaftler die Anzahl der möglichen Einsatzorte von etablierten Base-Editoren um 65 Prozent steigern. So können nun auch DNA-Sequenzen modifiziert werden, die bislang unerreichbar waren.
Durch die Optimierung der bestehenden Werkzeuge für die Genom-Editierung und ihrer ausgefeilten Anwendung ergeben sich ungeheuer vielfältige Möglichkeiten für die Grundlagenforschung sowie potenziell neue therapeutische Ansätze.
Joachim Wittbrodt
Die Forschungsergebnisse wurden in den Fachzeitschriften „eLife“ und „Development“ veröffentlicht. Die Forschungsarbeiten waren eingebunden in das Exzellenzcluster „3D Matter Made to Order“, das gemeinsam von der Universität Heidelberg und dem Karlsruher Institut für Technologie getragen wird. Der European Research Council, die Deutsche Forschungsgemeinschaft, das Deutsche Zentrum für Herz-Kreislaufforschung, die Deutsche Herzstiftung und die Joachim Herz Stiftung haben die Arbeiten und beteiligte Wissenschaftler gefördert.
Diese Newsmeldung wurde mit Material der Universität Heidelberg via Informationsdienst Wissenschaft erstellt.